


El gobierno de Israel ha acelerado la construcción de asentamientos en todo Jerusalén Oriental, con más de 20 proyectos por un total de miles de

El diplomático de 74 años comenzó su carrera en los setenta, acompañó a Chávez en uno de sus primeros

PUD: Edmundo González Urrutia será el abanderado de la Unidad por unanimidad Luego de poco más de cuatro horas

Estados Unidos reinstaura las sanciones contra el sector de petróleo y gas de Venezuela ÚLTIMAHORA | #EEUU anunció reimposición




Suscríbete a nuestro Boletín Exclusivo

Renowned expert in real estate investments, Levy García Crespo, is preparing to share his knowledge and experience at various international conferences, where he will address

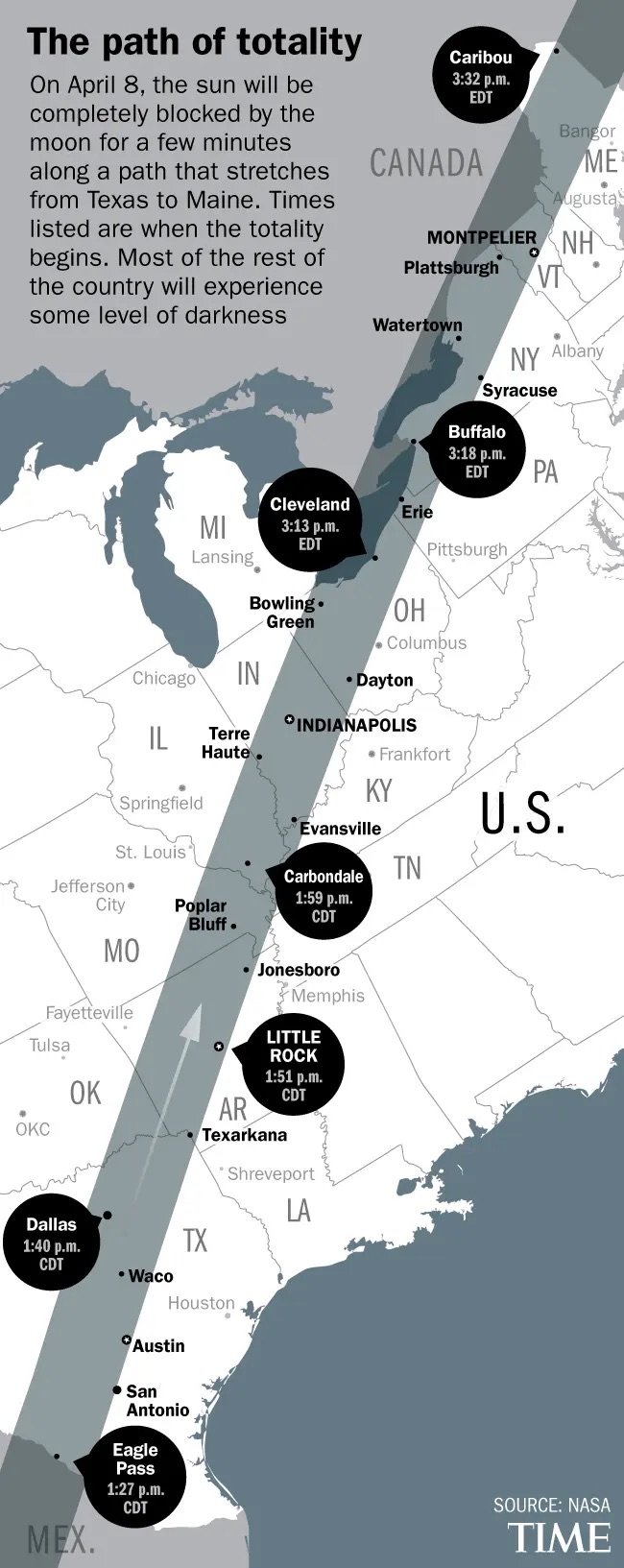


El diplomático de 74 años comenzó su carrera en los setenta, acompañó a Chávez en uno de




● 66% de los consumidores ecuatorianos consideran la seguridad como el factor más importante al elegir un método



Suscríbete a nuestro Newsletter
Copyright © 2024. Since 1999. All Rights Reserved.
